什么是De Novo全基因组测序
从头测序,也称为全基因组测序,是指在没有任何先前参考序列信息的情况下对生物体进行测序的过程。通过组装和比对等生物信息学分析方法,可以获得该物种的基因组序列。通过使用全基因组从头测序技术,可以获得动物、植物、细菌和真菌的完整基因组序列,从而推进这些物种的研究。一旦完成全基因组序列,就可以构建该物种的基因组数据库,为该物种的后基因组研究提供一个高效的平台,并为后续的基因挖掘和功能验证提供DNA序列信息。通过使用下一代高通量测序技术,可以高效且经济地获得所有物种的基因组序列,包括动物、植物、细菌和真菌,从而促进对这些物种的研究。
我们的De Novo全基因组测序服务
CD Genomic offers a one-stop solution for de novo genome sequencing services, covering experimental design, sample preparation, sequencing, and bioinformatics analysis, aiming to provide genomic solutions for your research. Our de novo genome sequencing services include:
动植物基因组的从头测序。
宏基因组的从头测序。
我们的De Novo全基因组测序服务优势
平台优势:获得高质量的基因组图谱
深度测序:精度高数据分析内容丰富:
标准分析、高级分析、定制分析在基因组测序和分析方面拥有丰富的经验:
成功完成多项大规模基因组测序项目
定制化基因组测序解决方案:可根据具体要求定制个性化基因组测序解决方法。
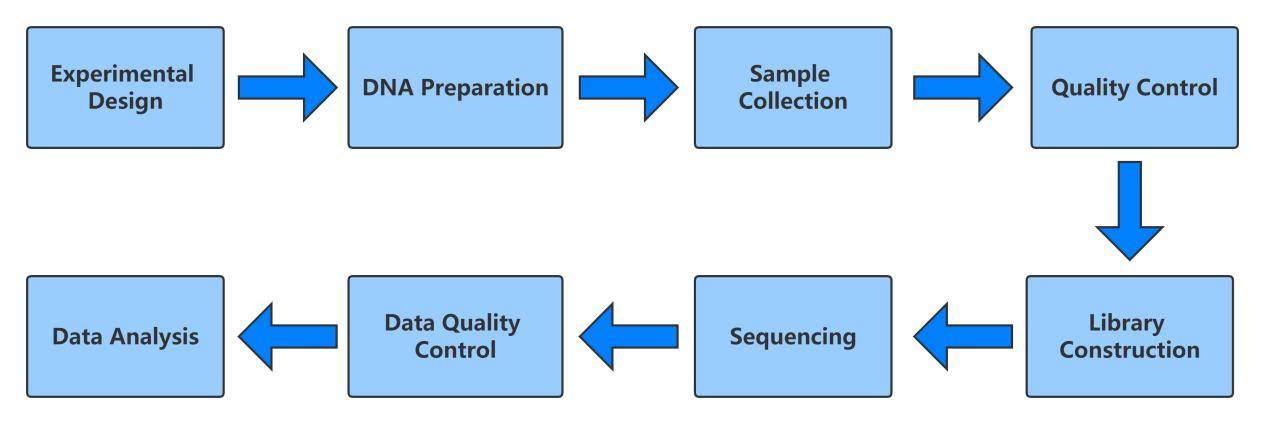
De Novo全基因组测序工作流程
生物信息学分析
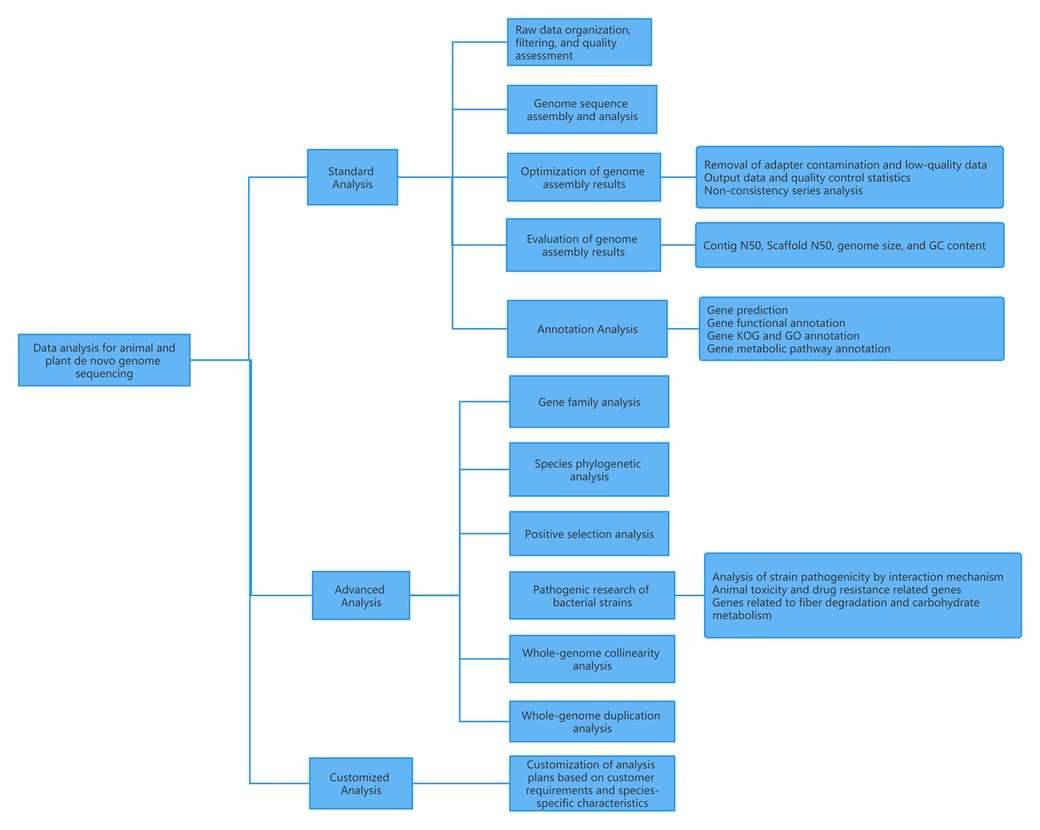
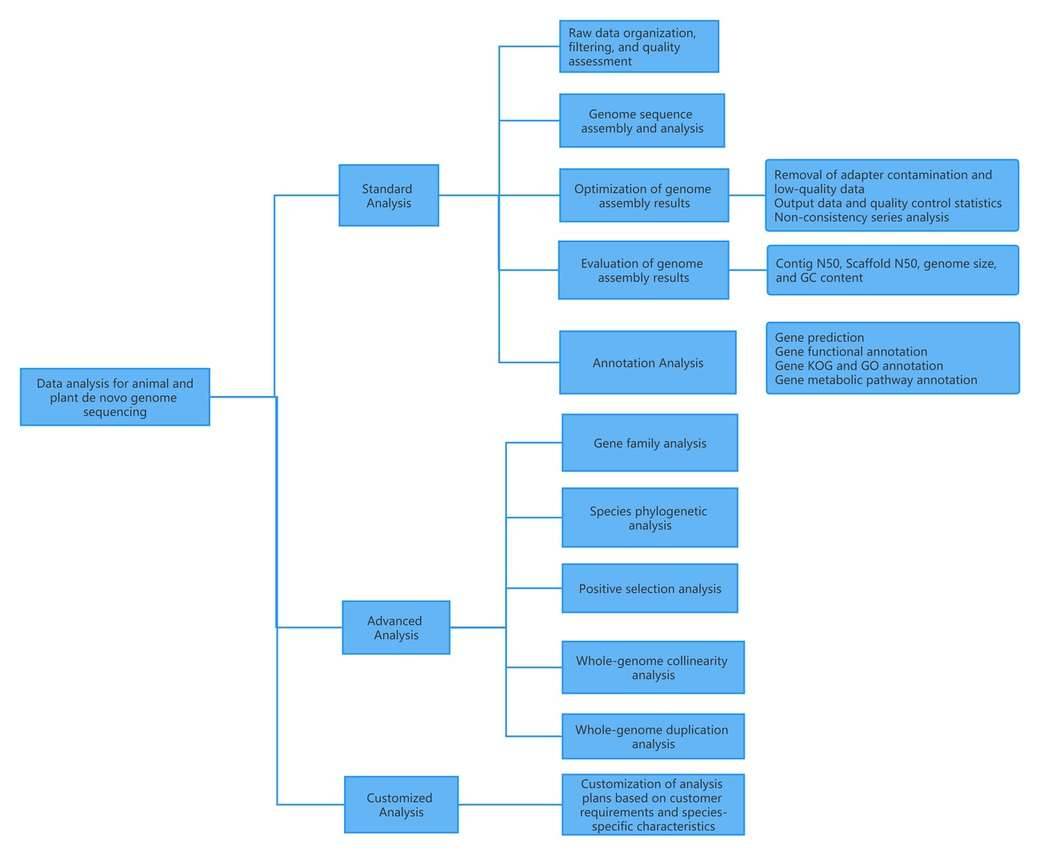
I.动植物从头基因组测序的数据分析
二、细菌和真菌从头基因组测序的数据分析
测序平台与策略
Illumina HiSeq X Ten、PacBio SMRT或牛津纳米孔。
Depth of coverage ≥ 100x.
More than 80% of bases with a ≥Q30 quality score.
配对端库和配对对库都可以在库准备步骤中构建。
样品要求
| 服务 | 样本类型 | 推荐数量 | 最低数量 | 最小浓度 |
| 全基因组测序(Illumina) | 基因组dna | ≥ 500 ng | 200纳克 | 10 ng/µL |
| 全基因组测序(无PCR) | 基因组dna | ≥ 1 µg | 500纳克 | 20 ng/µL |
| 全基因组测序(PacBio) | 基因组dna | ≥ 3 µg | 80 ng/µL | |
| 全基因组测序(纳米孔) | 基因组dna | ≥ 5 µg | 20 ng/µL |
1.比较基因组分析
使用progressive Mauve软件,对9株大肠杆菌O104:H4分离株的染色体序列进行比对,以显示移动遗传元件和基因组可变区的信息。通过利用核心SNP(单核苷酸多态性)位点信息,构建最大似然系统发育树,揭示菌株之间的进化关系。
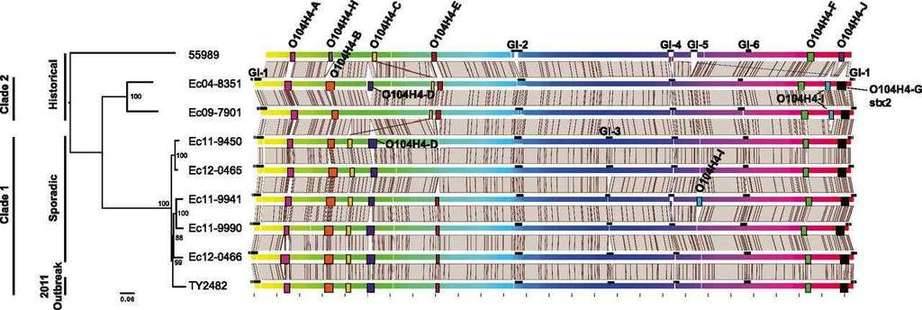 (Grad,Yonatan H.等人,2013)
(Grad,Yonatan H.等人,2013)
2.重复序列分析
采用从头预测和基于数据库的比对两种方法来分析纳塔尔长角甲虫和丹普伍德白蚁基因组序列中的转座因子(TE)。使用RepeatModeler软件对两种方法的结果进行整合和分析,以构建一个转座因子序列数据库。RepeatClassifier软件用于对转座因子进行分类。计算了两种白蚁基因组中转座因子的序列变异率,以揭示基因组扩展的潜在机制。
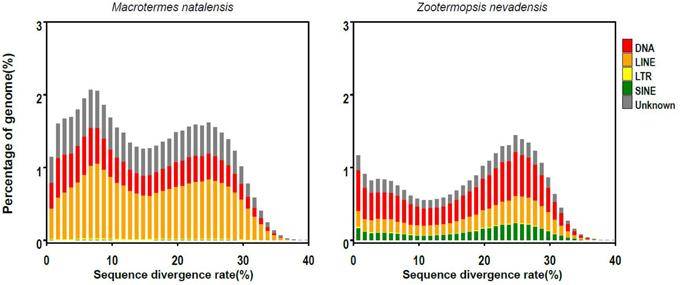 (科尔布、朱迪思等人,2015)
(科尔布、朱迪思等人,2015)
3.代谢途径
基于无限制脱氯细菌(PER-K23)的基因组注释信息,预测喹啉类化合物的生物合成涉及四种代谢途径。
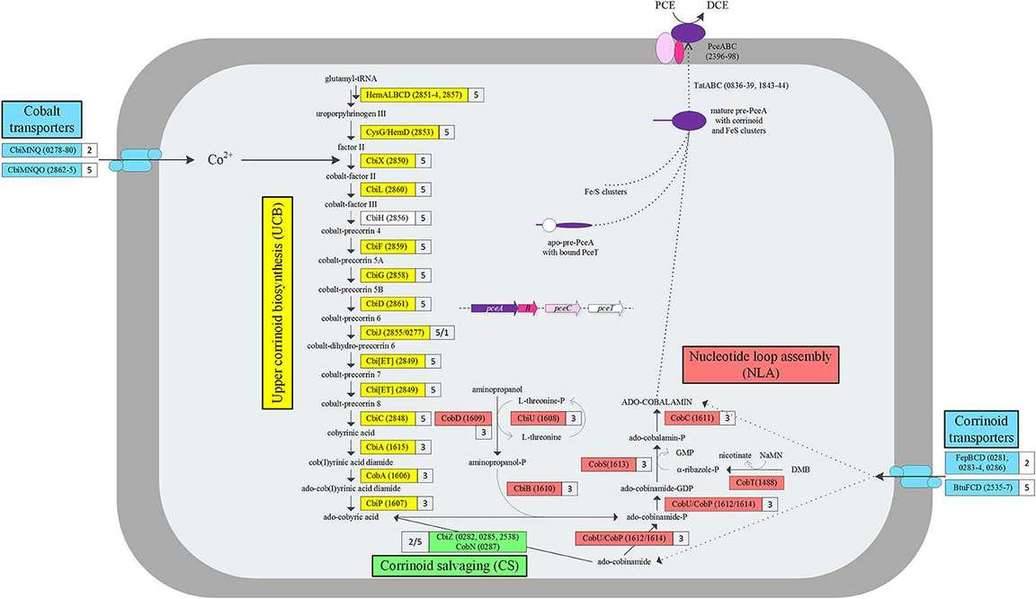 (Rupakula、Aamani等人,2014)
(Rupakula、Aamani等人,2014)
4.基因进化分析
利用117个单拷贝直系同源蛋白的基因序列,构建了软体动物、盐胞菌和厚壁菌门菌株的最大似然物种系统发育树。该分析揭示了不同细菌菌株基因组中mreB和fib基因的获得和丢失。
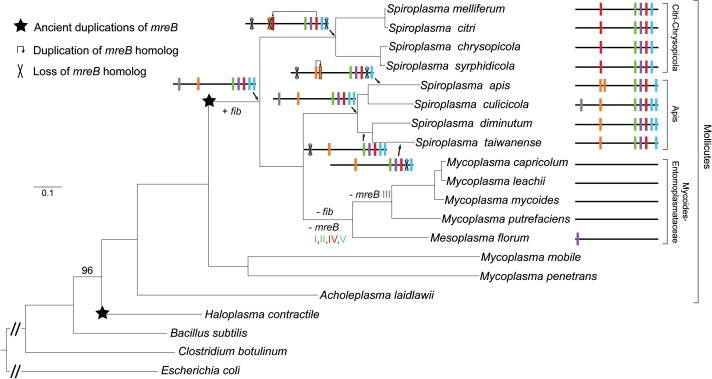 (库、川、罗文穗、郭志宏,2014)
(库、川、罗文穗、郭志宏,2014)

